毛竹长末端重复序列反转录转座子的全基因组特征及进化分析
陈娅欣,周明兵
(浙江农林大学 省部共建亚热带森林培育国家重点实验室,浙江 杭州 311300)
转座子(transposable elements, TEs)是一种自私的基因组“寄生虫”,能够增加拷贝数并改变其在宿主基因组中的位置[1]。转座子由于具有突变的可能,会对邻近基因表达产生潜在的危害,并导致染色体重排,对基因组的稳定性构成威胁[2−4]。转座子根据其转座中间产物被分为2类,其中Ⅰ类转座子包括复制黏贴式反转录转座子(retrotransposons, REs)[5],Ⅱ类转座子包括剪切黏贴式转座子[6]。Ⅰ类转座子根据其内部的结构可以分为 LTR类(long terminal repeat retrotransposons)[6]、DIRS类 (dictyostelium intermediate repeat sequence elements)[7]、PLE类 (penelope-like elements)[8]、LINE类 (long interspersed nuclear elements)[9]、SINE类(short interspersed nuclear elements)[10]。其中LTR反转录转座子是至今为止研究最多的一类[6]。LTR反转录转座子具有4个结构特点。第一,在序列两端有1对靶位点重复序列(target site repeats,TSD),约4~6 bp[11];第二,5′端和3′端有1对长为几十到几千bp不等高度相似的长末端重复序列[12];第三,LTR主要包括GAG衣壳蛋白编码区和POL多蛋白编码区(polyprotien),其中POL包括RH核糖核苷酸酶(ribonuclease h,RNaseH)、RT反转录酶(reverse transcriptase)、INT整合酶(integrase)和AP蛋白酶(aspartic proteinase)。还有一些Retrovirus和ENV超家族(superfamily)的LTR含有ENV序列(envelope protein, EN或ENV)[13];第四,在5′端附近有1个引物结合位点(primer binding site,PBS),可调控其基因组RNA反转录所必需的tRNA引物,它以染色体外线性DNA(extrachromosomal linear DNA, eclDNA)的形式产生LTR反转录转座子生命周期中间体。在3′端附近有1个富嘌呤位点(poly purine trait,PPT)[14],协助反转录的完成。根据LTR反转录转座子开放阅读框(open reading frames,ORF)的完整性分为自主LTR反转录转座子和非自主LTR反转录转座子[15]。自主LTR反转录转座子又可以根据POL中RT、INT和RH编码序列的排列方式,分为Ty1-copia 超家族(5′-INT-RT-RH-3′)和Ty3-gypsy超家族(5′-RH-RH-INT-3′)[16]。根据每个超家族的序列同源性(80-80-80的分类规则[17])可以分为不同的家族。根据LTR反转录转座子的同源性、蛋白结构、进化关系可以划分为不同的谱系,如梨Pyrus基因组中 被划分为 Ale、Ivana、Bianca、Angela、Tar、Tat、Athila、Renia、Crm、Galadriel、Tekay等11个谱系[18]。LTR反转录转座子的活性包括转录活性和转座活性。转录是转座的第1步,许多LTR反转录转座子在植物杂交、多倍体化或在环境挑战下发生去甲基化,被转录激活[19]。转座活性不仅包括转录活性,还受转录后调控,如植物基因组为了抑制转座子的活性通过转录基因沉默(transcriptional gene silencing, TGS)机制抑制它们的能力[20]。如果TGS得到缓解,则受21~22个核苷酸作用的转录后基因沉默机制(post-transcriptional gene silencing, PTGS)会将靶向转座子转录物进行降解[21],所以在实验条件下LTR反转录转座子很难被转座激活。在整个植物王国中LTR反转录转座子的进化特别成功,不断复制转座,导致基因组大小增加,基因组尺寸产生差异。在被子植物基因组之间由于几个LTR反转录转座子家族的扩增,产生一些巨大的基因组。例如2 400 Mb玉米Zeamays[22]和400 Mb水稻Oryzasativa[23]的基因组中LTR反转录转座子家族数相同,但是玉米基因组中5个谱系的LTR反转录转座子拷贝数较高。即使是亲缘关系很近的品种,LTR反转录转座子也会促使它们的基因结构产生巨大差异。如玉米与大刍草Zeamexicana是近亲,但是大刍草的基因组比玉米大1倍[24]。LTR反转录转座子在植物基因组中处于动态变化的过程,不仅会扩增,也会丢失,不平衡重组(illegitimate recombi nation)和非法重组(unequal recombination)活动就是丢失的主要原因[25−26]。不平衡重组和非法重组的产物主要包括含有TSD位点的solo LTR,不含TSD位点的Truncated LTR[27]。预测LTR反转录转座子可以通过4种方式[28]:比较基因组法(comparative genomic methods)[29]、重复序列从头算起法(de novo repeat discovery)[30]、同源比对法 (homology-based methods)[31]、基于结构预测法 (structure-based methods)。基于结构预测法是通过LTR反转录转座子的序列结构和转座机制分析来捕获,如LTR_STRUC、LTR_FINDER、LTRharvest、LTR_par、LTR_Rho等[32]。毛竹Phyllostachysedulis具有较高的经济和生态价值,其种植面积在中国的竹子总种植面积(443 万hm2)中占73.76%[33]。2018年第2版毛竹基因组的公布[34]为深入分析毛竹基因组中LTR反转座子提供了良好的条件。本研究运用了LTRharvest的方法[35],对第2版毛竹基因组中的LTR反转录转座进行预测,并对LTR反转录转座子的结构、在基因组中的分布特征、插入时间等进行系统分析,以期能了解毛竹LTR反转录转座子对基因组的影响。
1 材料与方法
1.1 毛竹LTR反转录转座子的鉴定与分类
第2版毛竹基因组序列、基因组注释文件来自毛竹基因组数据库(http://bamboo.bamboogdb.org/#/download)[34]。先利用LTRharvest软件[35]预测毛竹基因组LTR反转录转座子,利用cd-hit根据80-80-80的分类规则[17]进行序列同源性聚类,然后利用LTRdigestion[36]注释各个LTR反转录转座子结构域。接着根据LTR反转录转座子的POL编码区RT、INT和RH的顺序将其分为Ty1-Copia(INT-RT-RH)和Ty3-Gypsy (RT-RH-INT)2个超家族[16]。根据序列中的GAG和POL编码区与Gypsy Database 2.0网站中(http://gydb.org/index.php/Phylogeny: POL_LTR_retroelements)植物典型的 Tork、Reftrofit、Sire、Oryco、Del、Reina、Crm、Tat、Galadriel和Athila 谱系对应编码区的同源性,进一步将2个超家族分为10个谱系[35]。最后利用RepeatMakser软件分析LTR反转录转座子在毛竹基因组中的含量[31]。
1.2 毛竹LTR反转录转座子插入时间计算
使用MA等[37]对每条结构完整的毛竹LTR反转录转座子的插入时间进行计算:①对每条结构完整的LTR反转录转座子的两端LTR序列利用MUSCLE软件[38](使用默认参数)进行比对;②利用JUCKESCANTOR的方法[39]计算碱基突变频率(K);③利用公式T=K/(2r)计算插入时间,T表示时间,r表示生物钟,r=1.3×10−8bp·a−1[37]。
2 结果与分析
2.1 毛竹中LTR反转录转座子的鉴定和分类
由表1所示:得到1 014 565条LTR反转录转座子,占整个毛竹基因组的54.97%。毛竹中LTR反转录转座子比例与其他基因组相比,低于玉米基因组的70.1%[22],相近于高粱Sorghumbicolor基因组的55%[40],远高于水稻基因组的26%[23]。其中两端具有完整LTR序列,编码结构域完整的LTR反转录转座子(full-length LTR)有7 731条,两端具有完整LTR序列,编码结构域不完整的LTR反转录转座子(solo LTR)有13 656条(其余不含TSD位点的LTR反转录转座子忽略不计)。然后按照WICKER等[16]提出的真核生物转座子的分类方法,将blastn(all-vs-all)的方法和80-80-80的规则相结合,对7 731条完整的LTR反转录转座子进行分类,共分为1 562个家族。
毛竹LTR反转录转座子分为Ty1-copia和Typ3-gypsy 2个超家族,在1 562个LTR反转录转座子家族中有819个家族属于Ty1-Copia 超家族,共包括433 137条序列,长度为400 788 135 bp,占毛竹基因组的21.01%。743个家族属于Ty3-Gypsy超家族,共包括581 429条序列,长度为647 905 081 bp,占毛竹基因组的33.96%(表2)。Ty3-gypsy与Ty1-copia数量之比为1.3∶1.0,低于大豆Glycinemax(1.4∶1.0)[19]和玉米 (1.6∶1.0)[22],远低于水稻 (4.9∶1.0)[41]和高粱 (3.7∶1.0)[40],但远高于苜蓿Medicagosativa(0.3∶1.0)[42]。
根据LTR反转录转座子不同家族之间的进化关系和结构特征,Ty1-copia超家族和Ty3-gypsy超家族可以被分为多个不同的谱系[42−43]。根据Gypsy Database2.0[37]中植物典型的谱系序列特征,对毛竹LTR反转录转座子进行分类,将Ty1-copia超家族分为4个谱系,分别为Tork、Retrofit、Sire、Oryco;Ty3-gypsy超家族分为6个谱系,分别为Del、Reina、Crm、Tat、Galadriel、Athila。其中Tork包含236个家族,Reftrofit包含342个家族,Sire包含136个家族,Oryco包含105个家族,Del包含207个家族,Reina包含249个家族,Crm包含47个家族,Tat包含238个家族,Galadriel包含1个家族,Athila包含1个家族。在Ty1-copia超家族的4个谱系中,Sire的含量最高(达11.01%),紧随其后的是Tork(6.51%)。在 Ty3-gypsy超家族的 4个谱系中,Del的含量最高 (达 17.51%),紧随其后的是Tat(12.06%)(表1)。Tat和Del在植物中普遍存在并且是植物所特有的。ENV域在Sire中被识别,CHR域在Del和Reina中被识别(表1~2)。
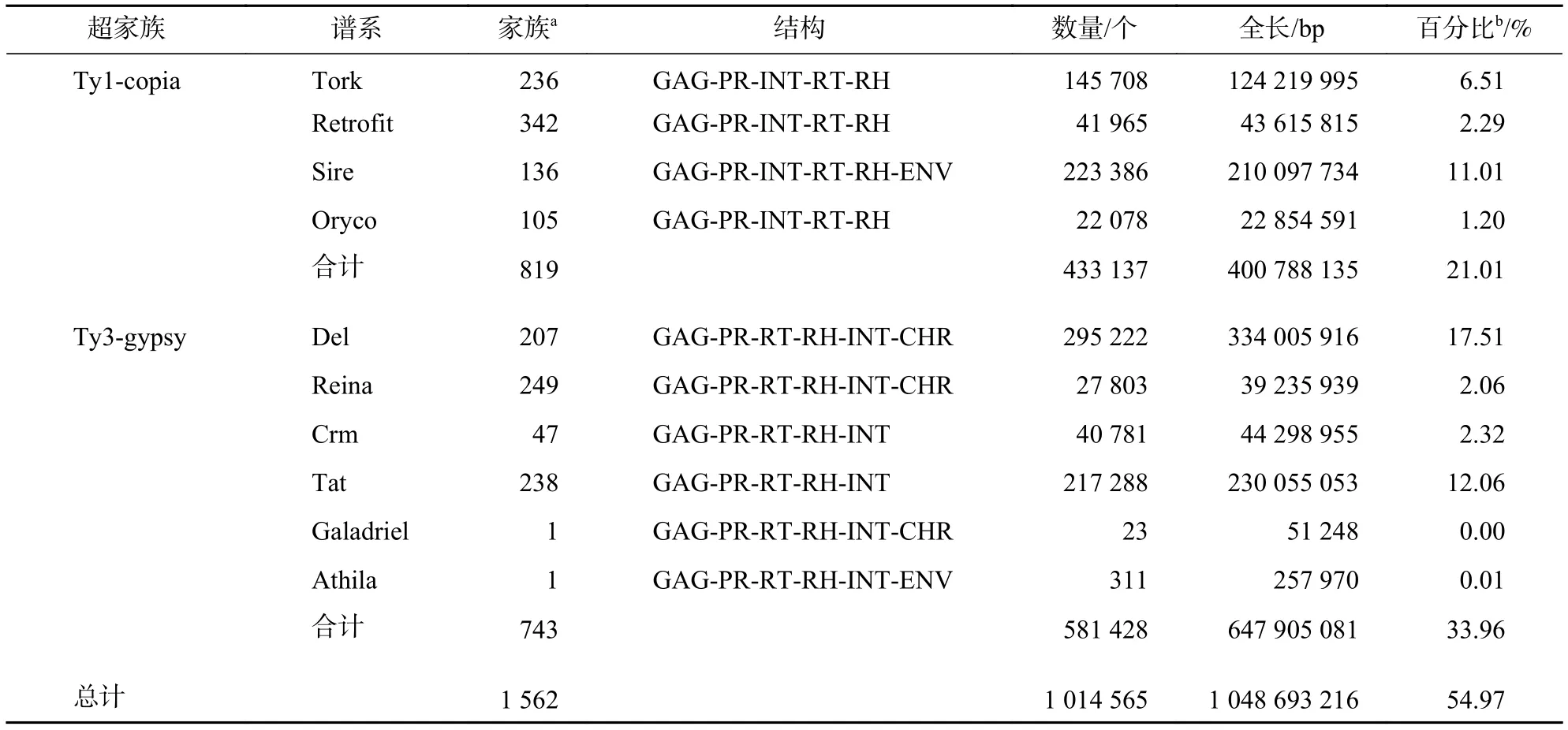
表 1 毛竹 LTR 反转录转座子超家族分类Table 1 Classification of LTR retrotransposons superfamily of moso bamboo genome
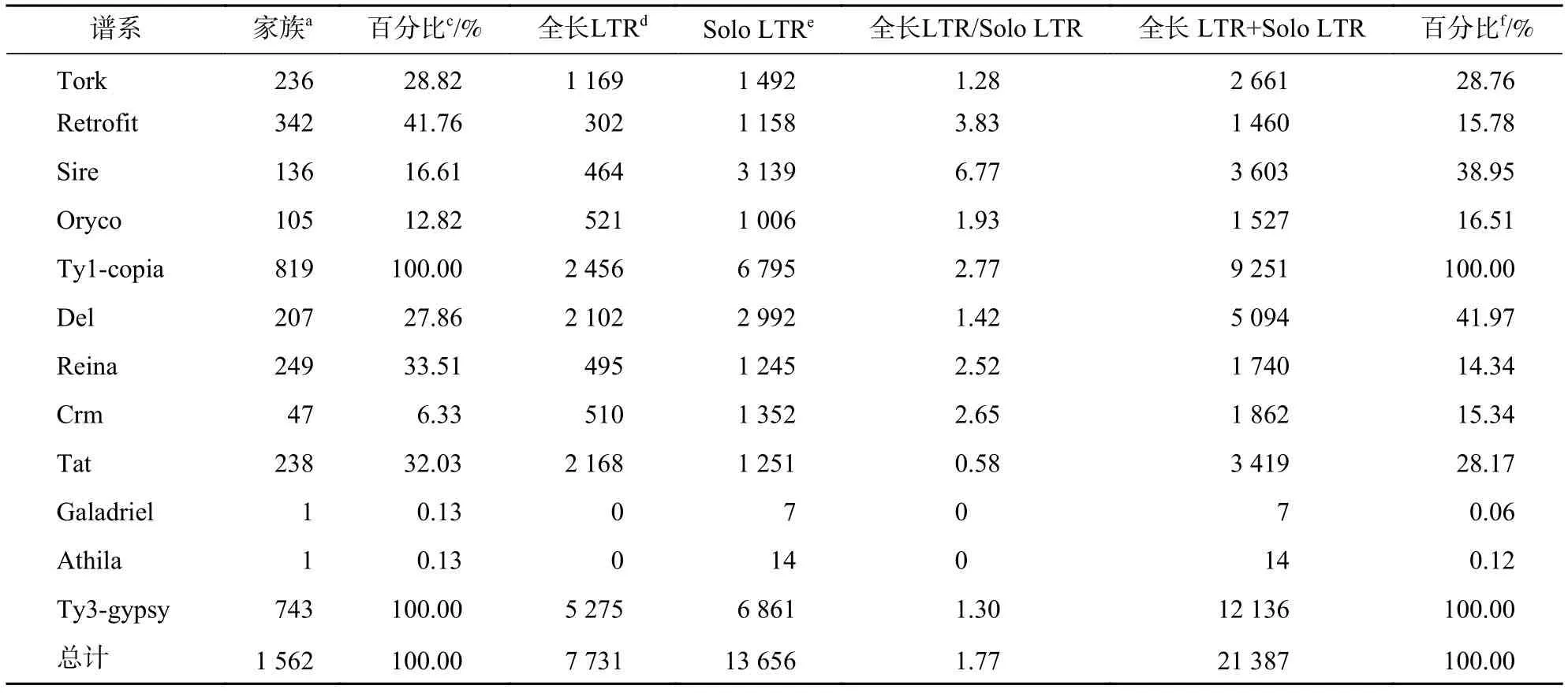
表 2 毛竹 LTR 反转录转座子谱系特征Table 2 Structure of LTR retrotransposon family of moso bamboo
2.2 毛竹LTR反转录转座子的PBS偏好性及LTR序列长度分析
在转座过程中,PBS是LTR反转录转座子反转录开始的重要位点,因为LTR反转录转座子开始反转录时tRNA会结合到RNA的PBS处,然后通过反转录酶合成cDNA[45]。不同超家族和谱系的LTR反转录转座子对PBS具有不同的偏好性。由表3所示:MetCAT24是转座子反转过程中使用频率最高的PBS位点,占4.05%,比其他的位点要高,其次是LysTTT和LysTTT10。表3中Ty1-copia和Ty3-gypsy超家族对PBS位点的偏好性呈相反趋势,MetCAT24是Ty1-copia超家族中使用最多的PBS位点,LysTTT是Ty3-gypsy超家族使用最多的PBS位点,但在Ty1-copia超家族中频率很低,仅有1个。LTR序列是LTR反转录转座子中特有的,它们位于LTR反转录转座子的5′端和3′端,是一对高度相似的序列,通常较长的LTR反转录转座子具有更长的LTR序列,结构也更加完整。所以把5′端LTR作为参照,对LTR序列长度进行统计,结果如图1显示。对LTR反转录转座子而言,LTR序列长度与其全长序列的长度成正比。
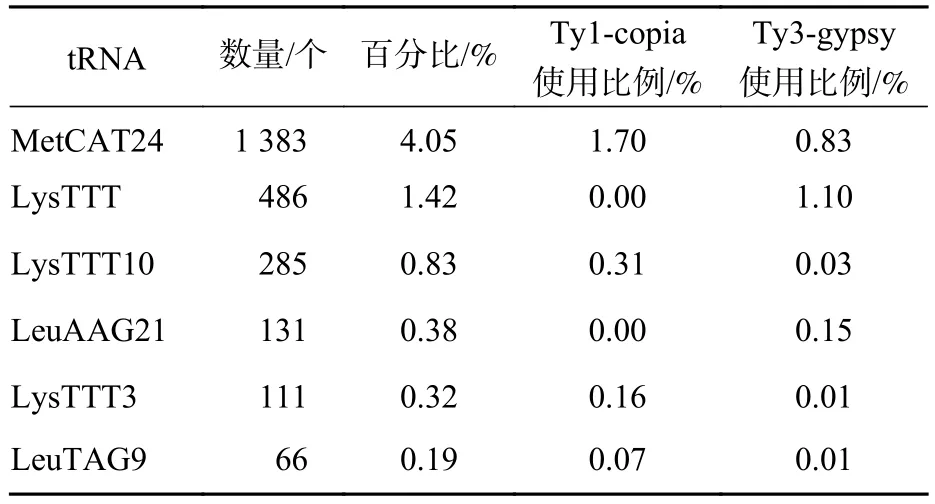
表 3 LTR 反转录转座子 PBS 使用统计Table 3 Usage status of PBS in LTR retrotransposons
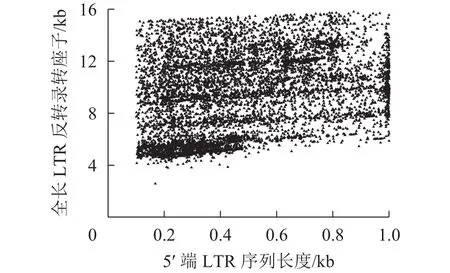
图 1 LTR反转录转座子全长与LTR序列长度的相关性Figure 1 Correlation of length between LTR and LTR retrotransposons
2.3 毛竹LTR反转录转座子的插入时间分布
对21 387个含有TSD位点的毛竹LTR反转录转座子的插入时间进行统计,如图2和图3所示。毛竹LTR反转录转座子的插入时间集中于0~2.0 Ma,其中插入最旺盛的是在1.0~1.5 Ma,有4 426 个,占21.06%,插入较少的是在3.0 Ma之前,有891个,仅占2.61%,插入时间为0的有508个(占1.4%),说明这部分LTR反转录转座子可能还具有转座潜力。Del转座频率最高,有4 777个拷贝,占22.62%,且在0.5~1.5 Ma转座活动最为旺盛,其次为Sire和Tat。而Retrofit、Oryco、Reina、Crm转座频率都较低,Retrofit最低,仅有1 527个拷贝,占6.91%。以上数据说明毛竹基因组中LTR反转录转座子在0~2.0 Ma内大量复制增长,且还处于不断增长的状态,但增长趋势在减弱。
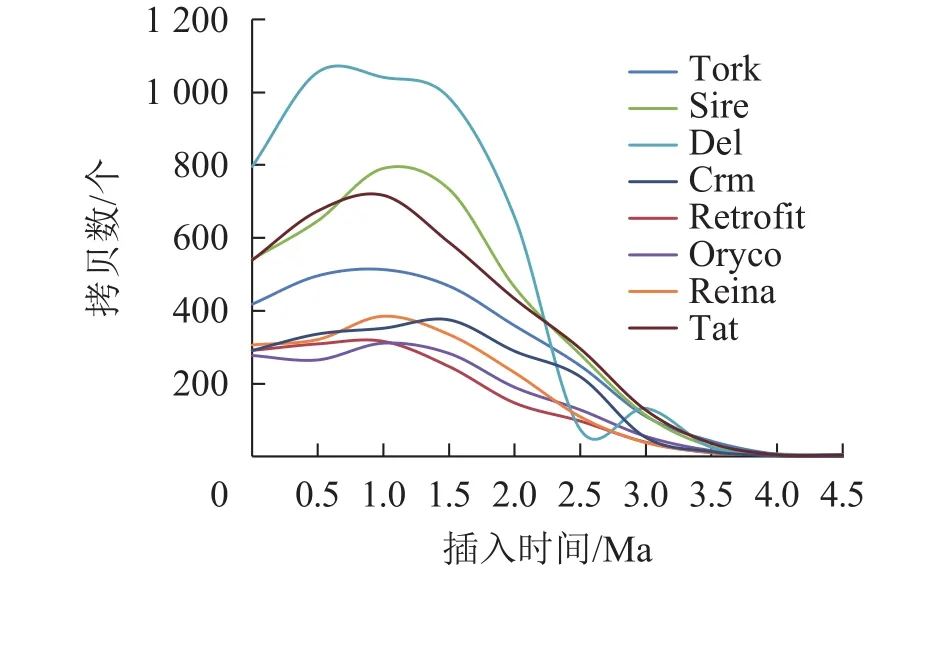
图 2 毛竹LTR反转录转座子各个谱系的插入时间Figure 2 Insertion time distribution of different lineages of moso bamboo LTR retrotransposons
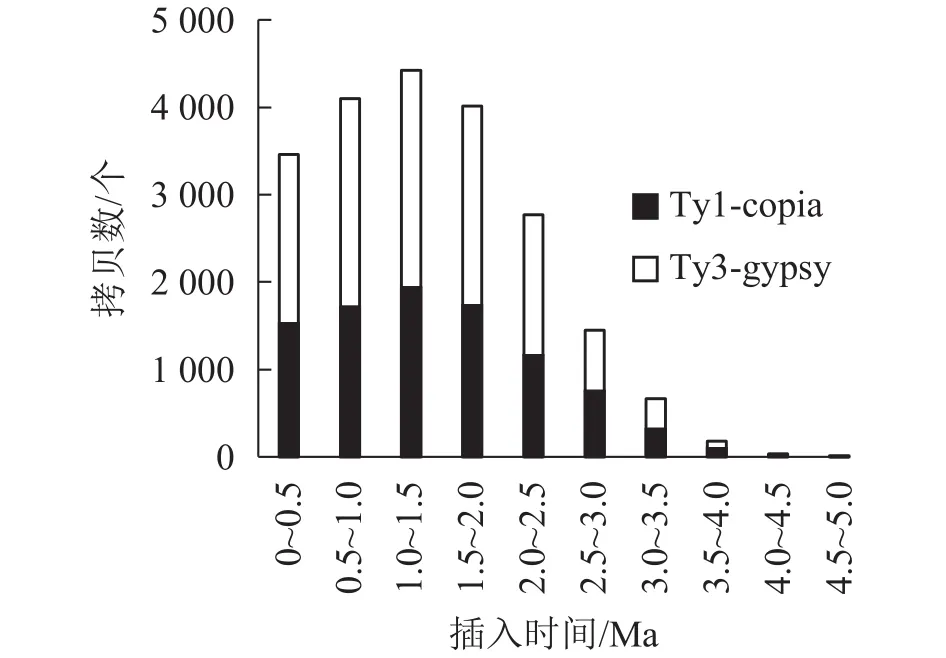
图 3 毛竹LTR反转录转座子超家族的插入时间Figure 3 Insertion times of superfumily of moso bamboo LTR retrotransposons
3 讨论
3.1 第2版毛竹基因组的公布提高有助于LTR反转录转座子准确鉴定
HU等[46]利用第1版毛竹基因组数据分析了LTR反转录转座子的分布结构和进化模式。但由于第1版毛竹基因组数据的碎片化严重,限制了对LTR反转录转座子的完整预测。毛竹第2版基因数据的覆盖范围、精准度都有所提高,完整性达95.2%[34],相比玉米(92.2%)[22]要高,与水稻(95.6%)[23]接近,所以本研究的结果准确性较高。然而,LTR反转录转座子是一种重复序列[47],软件无法准确逐条识别,产生假阴性。在不同的基因组中LTR反转录转座子所占的比例不同,如在酵母基因组中占3%[48],在玉米基因组中占70.1%[22],分布特点也有所差异,且基因组中还存在其他重复序列,所以也很容易产生假阳性。因此,利用较完整的毛竹第2版基因组,能在一定程度上避免误差。
在本研究中,通过对第2版毛竹基因组的注释共得到1 014 565条LTR反转录转座子(表1),占基因组的54.7%,较对第1版毛竹基因组注释的结果(1 954 616,39.83%,不包括未知LTR)数量有所下降,比例有所上升。对7 731条结构完整的LTR反转录转座子进行家族分类,共划分为1 562个家族,较第1版(959个)也有所上升。通过对LTR反转录转座子的结构完整性判断,solo-LTR较完整LTR反转录转座子比例更高(S/F为1.77),说明可能毛竹LTR反转录转座子不平衡重组和非法重组的活动频率较高,这可能是由于毛竹基因组在不断进化的过程中对转座子产生抑制,碎片化严重。但在第1版毛竹基因组中完整的LTR反转录转座子的占比更高(S/F为0.28),这是由于第1版基因组不完整所以信息显示不全面。总的来说,第2版毛竹基因组在转座子的注释、鉴定、家族和超家族的分类等方面都相比第1版毛竹基因组更加准确,但是依然存在数万条短的组装碎片,因此本研究对毛竹LTR反转录转座子的注释仍是保守值,随着毛竹基因组的更加完善会有更多的LTR反转录转座子被发现。
3.2 不同谱系的毛竹LTR反转录转座子在进化过程中具有不同的分化和扩增活性
根据Gypsy Database 2.0网站中植物典型的谱系序列特征,毛竹LTR反转录转座子共分为Sire、Oryco、Retrofit、Tork、Crm、Del、Reina、Tatol、Galadriel、Athila 等 10 个谱系。其中 Retrofit、Reina和Tat是数量最多的3个谱系。Galadriel和Athila在植物界中虽然广泛存在[15],但在毛竹基因组发现较少。一方面可能是Athila的大小通常为8.5~12.0 kb,并且具有相对较长的LTR序列(1.5~2.5 kb),很难被LTRhavest程序识别[35];另一方面,毛竹基因组的不完整和碎片化,可能会遗漏Galadriel和Athila。
将毛竹LTR反转录转座子的谱系与水稻[47]、拟南芥Arabidopsisthaliana[49]进行比较,发现毛竹的10个谱系包含了双子叶植物和单子叶植物共同的进化特征,这是它们分裂后分化的结果[50],其中Tork是例外,它在毛竹、水稻、拟南芥中并无明显差异,这表明Tork相对其他谱系更加保守。并且毛竹与水稻亚科在LTR反转录转座子都为多拷贝和多进化谱系并存,而拟南芥的谱系数则相对较少[49],这可能是由于不同进化速率导致的结果。
在不同谱系之间,LTR反转录转座子增殖差异较大。在毛竹Ty1-copia超家族中,Retrofit的LTR反转录转座子家族数量最多(342个),但拷贝数仅占15.78%,相比之下,Sire只有136个家族,拷贝数却达11.1%,占比最高。这种情况在Ty3-gypsy超家族更为显著,Reina包含249个家族,拷贝数却仅占2.06%,Crm只有47个家族,拷贝数所占比例比Reina还高一些。各谱系中LTR反转录转座子的数量反映了它们最近的扩增情况,而各谱系中家族的数量则代表了历史上不同的分化情况。因此,不同谱系的LTR反转录转座子在进化过程中具有不同的分化和扩增活性。
3.3 毛竹LTR反转录转座子插入时间主要集中在0~2.0 Ma
LTR反转录转座子两端的LTR序列是相同的,但在不断转座过程中,LTR序列会发生突变并分化,根据剪辑替换速率,可以得出LTR反转录转座子的插入时间[31]。毛竹LTR反转录转座子的插入时间在0~1.5 Ma呈直线式递增,但在大于1.5 Ma呈指数衰减,总体上呈现抛物线形式,与小麦Triticum aestivum[51]、桑树Morusnotabilis[52]类似,这说明毛竹LTR反转录转座子的插入时间主要集中于0~2.0 Ma,在1.5 Ma处于转座活动爆发期,但其增长趋势处于回缩的状态。
毛竹LTR反转录转座子在大于5.0 Ma区域缺失,可能原因:第一,5.0 Ma之前的老LTR反转录转座子与年轻的LTR反转录转座子发生重组,所以无法识别[42];第二,根据PENG等[33]的研究,在7.0~12.0 Ma中,毛竹基因组发生了四倍体事件,之后又不断进化为二倍体,在这个过程中毛竹基因组经历了较大的选择压力,所以5.0 Ma之前的毛竹LTR反转录转座子在基因组中被删除或严重破坏,无法通过结构预测和同源性比对来鉴定。

